2019年3月18日
人工知能が遊走する細胞を追跡する
成長中の赤ちゃんから高齢者まで、私たちの体は絶えず動き回る多くの細胞で構成されています。私たちが仕事のために会社に通勤するように、細胞もそれぞれの役割を果たすため、体内を遊走しています。これまで、細胞の遊走や形態の経時変化を定量化することは困難でしたが、この度沖縄科学技術大学院大学(OIST)で、それを可能にするツールが考案されました。
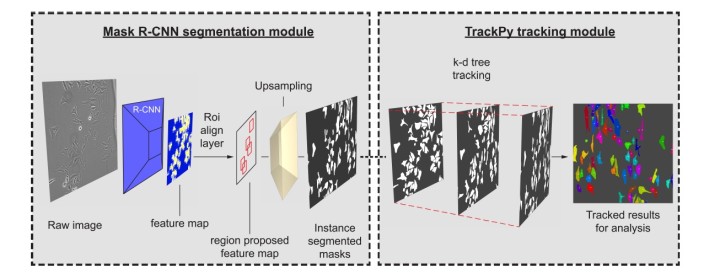
研究者らは、機械学習を用いて、遊走する細胞の顕微鏡画像を解析するソフトウェアをデザインしました。各細胞の形態変化を検知する、この革新的ソフトウェアは、琉球の方言で物体の輪郭をトレースする「透き写し」を意味する「ウシーガチ」と名付けられました。本論文は、2019年3月13日付けでSoftwareX誌に掲載され、使用方法の動画説明付きでオンライン上に一般公開されており、誰でも利用することができます。
母親の子宮の中では、胚の細胞が特定の位置まで遊走し、これにより手・足・臓器が正しい位置に形成されていきます。怪我をすると、免疫細胞が体内を駆け巡り、傷を治します。がんの転移は、がん細胞が体内を移動し、他の組織に腫瘍を形成することで起こります。新薬開発においては、投薬前と後の細胞の移動を記録、分析して、薬の効果を検証します。これらすべての分野に、今回開発されたウシーガチを応用することができるだけでなく、さらに他の分野への応用も期待されます。
「ウシーガチを使えば、細胞遊走のRAW画像から定量的データまで、まとめて得ることができます。」と、本論文の筆頭著者であるシェーフ・サイさんは説明します。サイさんは、エイミー・シェン教授が主宰するOISTマイクロ・バイオ・ナノ流体ユニットの学生であり、日本学術振興会(JSPS)のDC1特別研究員です。 「このような実験をコンピューターで行うには、現在の機能では不十分なため、通常は手作業で行います。しかし我々が考案したソフトウェアを使うと、少なくとも100倍のスピードで作業することが可能になります。」と、サイさんは説明を加えました。
同研究ユニット主宰者であり、本論文の責任著者であるエイミー・シェン教授は、次のように話します。「このソフトウェアが、学術界で活用されることを期待しています。生物学の研究や薬剤スクリーニングなど、様々な刺激に対する細胞の反応を追跡するあらゆる場面で、このソフトウェアを使うことができるでしょう。」
機械学習によって適応能力を得るウシーガチ
一般的には、顕微鏡下で細胞を観察するためには、染色液で染めるか、遺伝子を操作して、目の覚めるような色の蛍光ラベルを使用して発光させる必要があります。しかし、染色すると細胞の動きが変わるため、実験結果も歪められてしまいます。一方で、いわゆる「ラベルフリー」という手法を用いて、蛍光染色せずに細胞遊走の観測を試みる研究者もいますが、ラベルフリーで標識のない細胞は、顕微鏡画像の背景に溶け込んでしまい、既存のソフトウェアで解析することは非常に困難です。
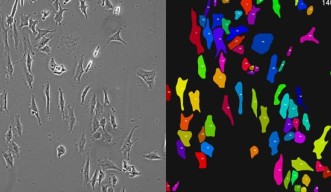
しかし、ウシーガチを使ってソフトウェアに学習させると、この問題は解決します。研究者が教師役になり、ソフトウェアに新たな画像を学習させ、細胞を区別させるのです。このプログラムの学習スピードは速く、新しいデータに即座に適応します。たとえ細胞同士が、東京の通勤電車内のようにすし詰め状態であったとしても、各細胞の動きを容易にトラッキングすることができるのです。
「既存のソフトウェアの多くは、密集した細胞を個別に識別することができず、塊として捉えます。しかしウシーガチの場合は、細胞同士が密着していても、一つひとつ分けて捉えることができるのです。実験の最初から最後まで、単一の細胞を追跡することが可能です。」とサイさんは説明します。個人のパソコンを使って、単一細胞レベルの解像度で、ラベルフリーの細胞の動きを解析するソフトウェアとしては、ウシーガチが、現存するソフトの中で最速です。
人間の脳を模倣するソフトウェア
研究者たちは、人間の脳を簡素化し、画像処理を行わせるイメージで、ウシーガチをデザインしました。このデザインにより、ソフトウェアが各細胞の輪郭をトレースし、瞬間ごとの動きをモニターして、情報を処理可能な数値に変換することができるようになりました。
本プログラムは、脳細胞の情報処理方法に類似した「畳み込みニューラルネットワーク」という機械学習の仕組みを用いています。人間の目は光を捉えると、ニューロンがそのシグナルを分析し、目に映る物体とその位置関係を認識します。ニューロンはまず、物体を大まかに描写し、情報を次のニューロンに伝え、この伝達を繰り返すうちに、画像はより詳細に描写されていきます。ニューラルネットワークも同じ仕組みですが、唯一の違いは、ここでの「ニューロン」は実際の細胞ではなく、コードの集合体であるということです。
ウシーガチは、人間の脳に類似したこのデザインのおかげで、正確性と適応性に優れているのです。開発した研究者たちは、今後、細胞の輪郭だけではなく、細胞内の構成要素を特定できるニューラルネットワークの開発を目指しています。そのようなツールがあれば、顕微鏡で様々な細胞が、正常か異常か、新しいか古いかを容易に判定すること、又は細胞系譜までを分析することができるかもしれません。ウシーガチのようなプログラムは、基礎生物学や生物工学の研究だけにとどまらず、その他の分野でも有用となる可能性があります。
報道関係のお問い合わせ